使用 PyTorch 和 TIAToolbox 进行整体切片图像分类¶
Created On: Dec 19, 2023 | Last Updated: Jun 04, 2025 | Last Verified: Nov 05, 2024
小技巧
为了充分利用本教程,我们建议使用此 Colab 版本,以便实验下面展示的信息。
介绍¶
在本教程中,我们将展示如何利用 PyTorch 深度学习模型和 TIAToolbox 来分类整体切片图像(WSIs)。WSI 是通过手术或活组织检查提取的人体组织样本的图像,并使用专业扫描仪进行扫描。这些图像被病理学家和计算病理学研究人员用于 研究癌症等疾病的微观水平,以便例如了解肿瘤生长并帮助改善患者的治疗。
处理 WSIs 的挑战在于其巨大的尺寸。例如,一个典型的切片图像的大小约为 100,000x100,000 像素,其中每个像素在切片上对应约0.25x0.25微米。这带来了加载和处理此类图像的挑战,更不用说在单个研究中处理数百甚至数千张WSI了(更大的研究能产生更好的结果)!
传统的图像处理管道不适用于WSI处理,因此我们需要更好的工具。而 TIAToolbox 可以提供帮助,它提供了一组实用工具,能够快速且高效地导入和处理组织切片。通常,WSI以金字塔结构保存,同一图像在不同放大级别的多个副本被优化以便于可视化。金字塔的第0级(或底层)包含最高放大或缩放级别的图像,而金字塔的较高层则是基础图像的低分辨率副本。下面展示了金字塔结构的草图。
|WSI金字塔堆栈| WSI金字塔堆栈 (来源)
TIAToolbox 允许我们自动化常见的下游分析任务,如 组织分类。在本教程中,我们将展示如何:1. 使用 TIAToolbox 加载 WSI 图像;2. 使用不同的 PyTorch 模型在切片级别对图像进行分类。在本教程中,我们将演示如何使用 TorchVision 的 ResNet18 模型以及自定义 HistoEncoder <https://github.com/jopo666/HistoEncoder>`__ 模型。
让我们开始吧!
设置环境¶
要运行本教程中提供的示例,需要以下软件包作为前提。
OpenJpeg
OpenSlide
Pixman
TIAToolbox
HistoEncoder(用于自定义模型示例)
请在终端中运行以下命令以安装这些软件包:
apt-get -y -qq install libopenjp2-7-dev libopenjp2-tools openslide-tools libpixman-1-dev pip install -q 'tiatoolbox<1.5' histoencoder && echo “安装完成。”
或者,你可以运行 brew install openjpeg openslide 来在 MacOS 上安装所需软件包,而不是使用 apt-get。更多安装信息可以在 此处找到。
运行前清理¶
为了确保适当的清理(例如异常终止时),此运行中下载或创建的所有文件都保存在单个目录 global_save_dir 中,我们将其设置为 “./tmp/”。为了简化维护,目录名称仅在此处出现,因此可以轻松修改。
warnings.filterwarnings("ignore")
global_save_dir = Path("./tmp/")
def rmdir(dir_path: str | Path) -> None:
"""Helper function to delete directory."""
if Path(dir_path).is_dir():
shutil.rmtree(dir_path)
logger.info("Removing directory %s", dir_path)
rmdir(global_save_dir) # remove directory if it exists from previous runs
global_save_dir.mkdir()
logger.info("Creating new directory %s", global_save_dir)
下载数据¶
对于我们的示例数据,我们将使用一张全切片图像以及来自 Kather 100k 数据集验证子集中的一些补丁。
wsi_path = global_save_dir / "sample_wsi.svs"
patches_path = global_save_dir / "kather100k-validation-sample.zip"
weights_path = global_save_dir / "resnet18-kather100k.pth"
logger.info("Download has started. Please wait...")
# Downloading and unzip a sample whole-slide image
download_data(
"https://tiatoolbox.dcs.warwick.ac.uk/sample_wsis/TCGA-3L-AA1B-01Z-00-DX1.8923A151-A690-40B7-9E5A-FCBEDFC2394F.svs",
wsi_path,
)
# Download and unzip a sample of the validation set used to train the Kather 100K dataset
download_data(
"https://tiatoolbox.dcs.warwick.ac.uk/datasets/kather100k-validation-sample.zip",
patches_path,
)
with ZipFile(patches_path, "r") as zipfile:
zipfile.extractall(path=global_save_dir)
# Download pretrained model weights for WSI classification using ResNet18 architecture
download_data(
"https://tiatoolbox.dcs.warwick.ac.uk/models/pc/resnet18-kather100k.pth",
weights_path,
)
logger.info("Download is complete.")
读取数据¶
我们创建一个补丁列表和一个对应的标签列表。例如,label_list 中的第一个标签将指示 patch_list 中第一个图像补丁的类别。
# Read the patch data and create a list of patches and a list of corresponding labels
dataset_path = global_save_dir / "kather100k-validation-sample"
# Set the path to the dataset
image_ext = ".tif" # file extension of each image
# Obtain the mapping between the label ID and the class name
label_dict = {
"BACK": 0, # Background (empty glass region)
"NORM": 1, # Normal colon mucosa
"DEB": 2, # Debris
"TUM": 3, # Colorectal adenocarcinoma epithelium
"ADI": 4, # Adipose
"MUC": 5, # Mucus
"MUS": 6, # Smooth muscle
"STR": 7, # Cancer-associated stroma
"LYM": 8, # Lymphocytes
}
class_names = list(label_dict.keys())
class_labels = list(label_dict.values())
# Generate a list of patches and generate the label from the filename
patch_list = []
label_list = []
for class_name, label in label_dict.items():
dataset_class_path = dataset_path / class_name
patch_list_single_class = grab_files_from_dir(
dataset_class_path,
file_types="*" + image_ext,
)
patch_list.extend(patch_list_single_class)
label_list.extend([label] * len(patch_list_single_class))
# Show some dataset statistics
plt.bar(class_names, [label_list.count(label) for label in class_labels])
plt.xlabel("Patch types")
plt.ylabel("Number of patches")
# Count the number of examples per class
for class_name, label in label_dict.items():
logger.info(
"Class ID: %d -- Class Name: %s -- Number of images: %d",
label,
class_name,
label_list.count(label),
)
# Overall dataset statistics
logger.info("Total number of patches: %d", (len(patch_list)))

|2023-11-14|13:15:59.299| [INFO] Class ID: 0 -- Class Name: BACK -- Number of images: 211
|2023-11-14|13:15:59.299| [INFO] Class ID: 1 -- Class Name: NORM -- Number of images: 176
|2023-11-14|13:15:59.299| [INFO] Class ID: 2 -- Class Name: DEB -- Number of images: 230
|2023-11-14|13:15:59.299| [INFO] Class ID: 3 -- Class Name: TUM -- Number of images: 286
|2023-11-14|13:15:59.299| [INFO] Class ID: 4 -- Class Name: ADI -- Number of images: 208
|2023-11-14|13:15:59.299| [INFO] Class ID: 5 -- Class Name: MUC -- Number of images: 178
|2023-11-14|13:15:59.299| [INFO] Class ID: 6 -- Class Name: MUS -- Number of images: 270
|2023-11-14|13:15:59.299| [INFO] Class ID: 7 -- Class Name: STR -- Number of images: 209
|2023-11-14|13:15:59.299| [INFO] Class ID: 8 -- Class Name: LYM -- Number of images: 232
|2023-11-14|13:15:59.299| [INFO] Total number of patches: 2000
正如你所看到的,这个补丁数据集中有9个类别/标签,ID从0到8,并有相关的类别名称,描述补丁中主要的组织类型:
BACK ⟶ 背景(空玻璃区域)
LYM ⟶ 淋巴细胞
NORM ⟶ 正常结肠黏膜
DEB ⟶ 碎屑
MUS ⟶ 平滑肌
STR ⟶ 与癌症相关的间质
ADI ⟶ 脂肪组织
MUC ⟶ 粘液
TUM ⟶ 结直肠腺癌上皮
分类图像补丁¶
我们演示如何先使用 patch 模式,然后使用 wsi 模式对数字切片中的每个补丁进行预测。
定义 PatchPredictor 模型¶
PatchPredictor 类运行一个基于 CNN 的分类器,使用 PyTorch 编写。
model可以是任何训练好的 PyTorch 模型,条件是它应该遵循tiatoolbox.models.abc.ModelABC(文档) <https://tia-toolbox.readthedocs.io/en/latest/_autosummary/tiatoolbox.models.models_abc.ModelABC.html>`__ 类结构。关于这一点的更多信息,请参阅 高级模型技术示例笔记本。为了加载自定义模型,你需要编写一个小的预处理函数,例如preproc_func(img),以确保输入张量格式正确,适用于加载的网络。或者,你可以将
pretrained_model作为字符串参数传递。这指定了执行预测的 CNN 模型,它必须是列出在 此处 的模型之一。命令将如下所示:predictor = PatchPredictor(pretrained_model='resnet18-kather100k', pretrained_weights=weights_path, batch_size=32)。pretrained_weights:使用pretrained_model时,相应的预训练权重默认也会下载。你可以通过pretrained_weight参数用自己的一组权重覆盖默认值。batch_size:每次输入模型的图像数量。该参数的较高值需要更大的(GPU)内存容量。
# Importing a pretrained PyTorch model from TIAToolbox
predictor = PatchPredictor(pretrained_model='resnet18-kather100k', batch_size=32)
# Users can load any PyTorch model architecture instead using the following script
model = vanilla.CNNModel(backbone="resnet18", num_classes=9) # Importing model from torchvision.models.resnet18
model.load_state_dict(torch.load(weights_path, map_location="cpu", weights_only=True), strict=True)
def preproc_func(img):
img = PIL.Image.fromarray(img)
img = transforms.ToTensor()(img)
return img.permute(1, 2, 0)
model.preproc_func = preproc_func
predictor = PatchPredictor(model=model, batch_size=32)
预测补丁标签¶
我们创建一个预测器对象,然后使用 patch 模式调用 predict 方法。我们随后计算分类准确率和混淆矩阵。
with suppress_console_output():
output = predictor.predict(imgs=patch_list, mode="patch", on_gpu=ON_GPU)
acc = accuracy_score(label_list, output["predictions"])
logger.info("Classification accuracy: %f", acc)
# Creating and visualizing the confusion matrix for patch classification results
conf = confusion_matrix(label_list, output["predictions"], normalize="true")
df_cm = pd.DataFrame(conf, index=class_names, columns=class_names)
df_cm
|2023-11-14|13:16:03.215| [INFO] Classification accuracy: 0.993000
为整个切片预测补丁标签¶
我们现在介绍 IOPatchPredictorConfig,它是一个指定图像读取和预测写入配置的类,用于模型预测引擎。这是为了通知分类器 WSI 金字塔的哪个级别应该被读取、处理数据以及生成输出。
IOPatchPredictorConfig 的参数定义如下:
input_resolutions:一个字典形式的列表,指定每个输入的分辨率。列表元素必须与目标model.forward()中的顺序相同。如果你的模型仅接受一个输入,则只需要放一个字典指定'units'和'resolution'。请注意,TIAToolbox 支持具有多个输入的模型。有关单位和分辨率的更多信息,请参阅 TIAToolbox 文档。patch_input_shape:最大输入的形状,以 (高度, 宽度) 格式。stride_shape:补丁提取过程中过两连续补丁之间的步幅大小。如果用户将stride_shape设置为patch_input_shape,补丁将被提取并处理而没有任何重叠。
wsi_ioconfig = IOPatchPredictorConfig(
input_resolutions=[{"units": "mpp", "resolution": 0.5}],
patch_input_shape=[224, 224],
stride_shape=[224, 224],
)
predict 方法将 CNN 应用于输入补丁上并获得结果。以下是参数及其描述:
mode:要处理的输入类型。根据你的应用选择patch、tile或wsi。imgs:输入列表,应为输入图块或 WSI 的路径列表。return_probabilities:设置为 True 以获取每个类别的概率以及输入补丁的预测标签。如果你希望合并预测以生成tile或wsi模式的预测地图,可以设置return_probabilities=True。ioconfig:使用IOPatchPredictorConfig类设置 IO 配置信息。resolution和unit``(下文未显示):这些参数指定 WSI 金字塔级别或每像素微米分辨率,根据我们计划提取补丁的内容,可以替代 ``ioconfig使用。在这里,我们将 WSI 级别指定为'baseline',即等同于第0级。通常,这是最高清分辨率的级别。在这个特殊情况下,图像只有一个级别。更多信息可以在 文档 中找到。masks:对应于imgs列表中 WSI 掩膜路径的列表。这些掩膜指定我们想要从原始 WSI 中提取补丁的区域。如果某个 WSI 的掩膜指定为None,则该 WSI 所有补丁(甚至是背景区域)的标签都将被预测。这可能会导致不必要的计算。merge_predictions:如果需要生成补丁分类结果的二维地图,你可以将此参数设置为True。然而,对于大型 WSI,这将需要大量的可用内存。一种替代(默认)解决方案是设置merge_predictions=False,然后使用你后面将看到的merge_predictions函数生成二维预测地图。
由于我们正在使用大型 WSI,补丁提取和预测过程可能需要一些时间(请确保在拥有支持 Cuda 的 GPU 和 PyTorch+Cuda 的情况下设置 ON_GPU=True)。
with suppress_console_output():
wsi_output = predictor.predict(
imgs=[wsi_path],
masks=None,
mode="wsi",
merge_predictions=False,
ioconfig=wsi_ioconfig,
return_probabilities=True,
save_dir=global_save_dir / "wsi_predictions",
on_gpu=ON_GPU,
)
通过可视化 wsi_output,我们可以看到预测模型在我们的全切片图像上的表现。我们首先需要合并补丁预测输出,然后将其作为原始图像上的叠加层进行可视化。与之前一样,merge_predictions 方法用于合并补丁预测。在这里,我们将参数 resolution=1.25, units='power' 设置为1.25倍放大率生成预测地图。如果你想要更高/更低分辨率(更大/更小)的预测地图,需要相应地更改这些参数。当预测被合并后,使用 overlay_patch_prediction 函数将预测地图叠加到WSI缩略图上,该缩略图应根据预测合并所用的分辨率提取。
overview_resolution = (
4 # the resolution in which we desire to merge and visualize the patch predictions
)
# the unit of the `resolution` parameter. Can be "power", "level", "mpp", or "baseline"
overview_unit = "mpp"
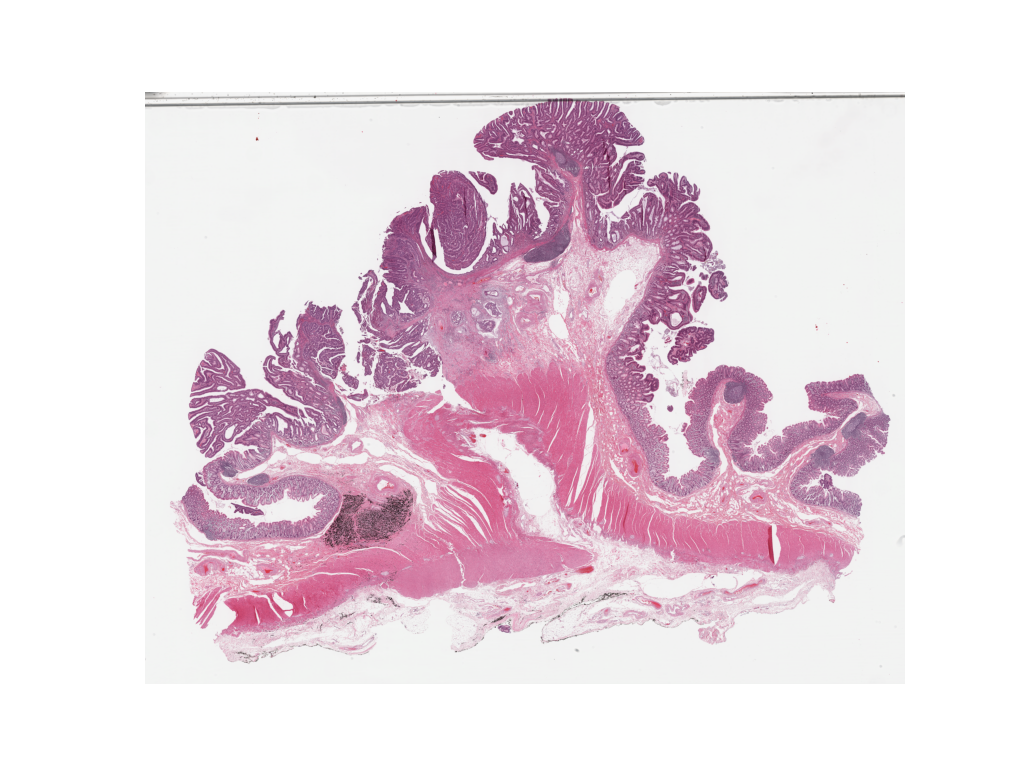
wsi = WSIReader.open(wsi_path)
wsi_overview = wsi.slide_thumbnail(resolution=overview_resolution, units=overview_unit)
plt.figure(), plt.imshow(wsi_overview)
plt.axis("off")
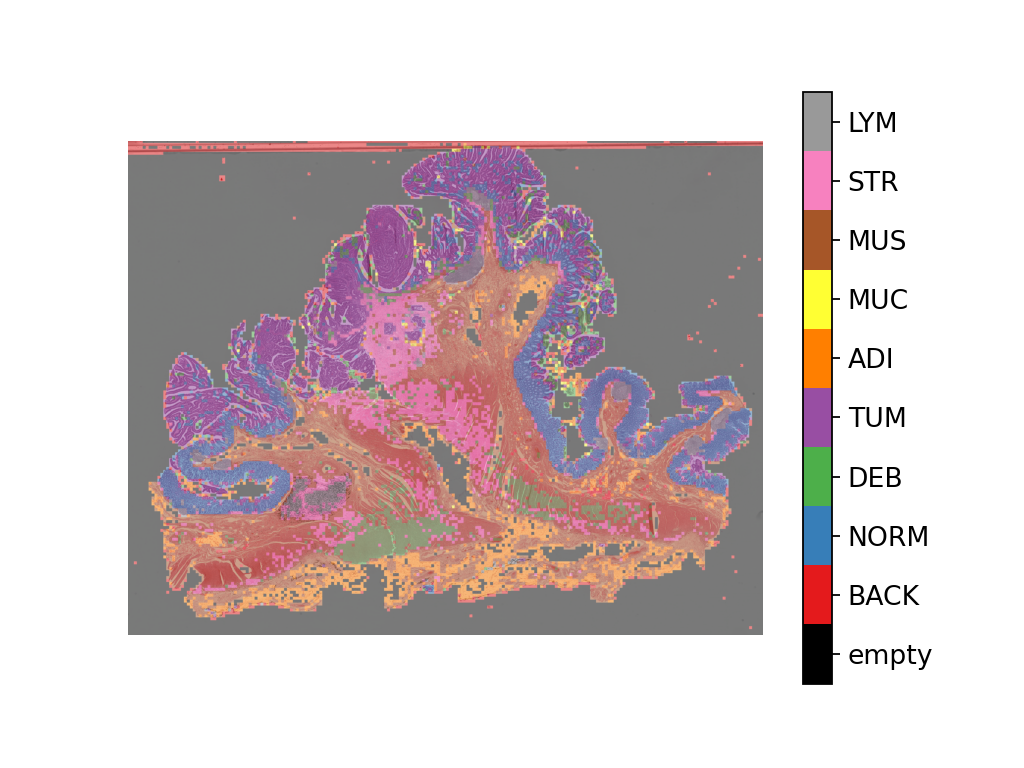
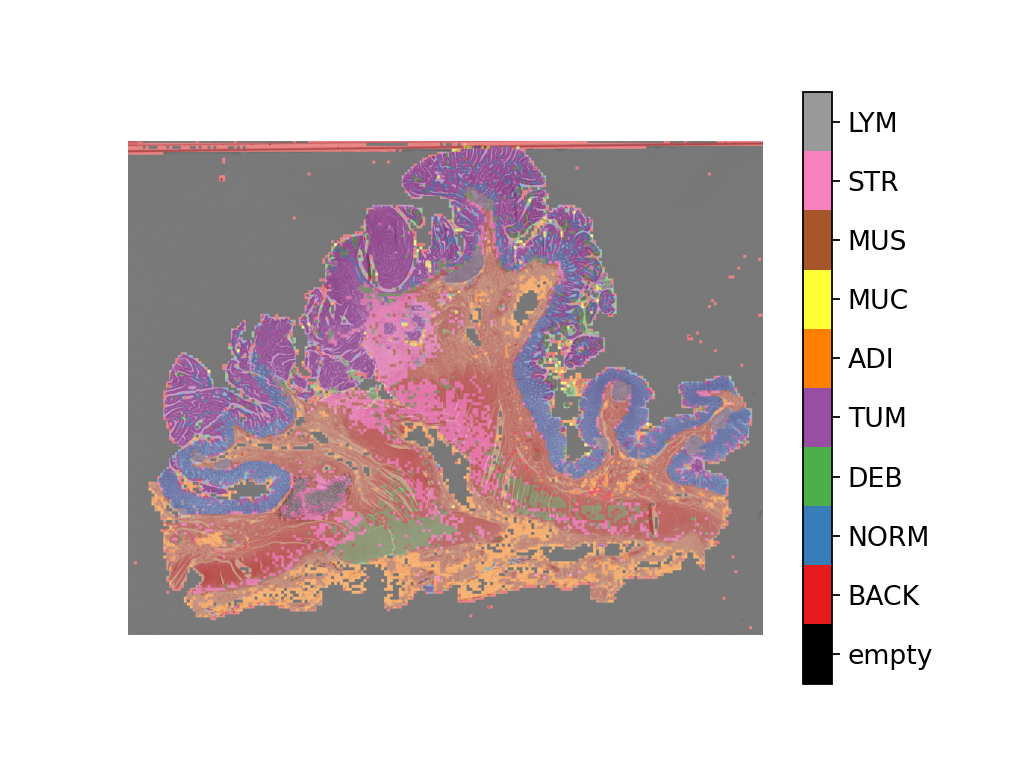
将预测地图叠加到此图像中,如下所示:
# Visualization of whole-slide image patch-level prediction
# first set up a label to color mapping
label_color_dict = {}
label_color_dict[0] = ("empty", (0, 0, 0))
colors = cm.get_cmap("Set1").colors
for class_name, label in label_dict.items():
label_color_dict[label + 1] = (class_name, 255 * np.array(colors[label]))
pred_map = predictor.merge_predictions(
wsi_path,
wsi_output[0],
resolution=overview_resolution,
units=overview_unit,
)
overlay = overlay_prediction_mask(
wsi_overview,
pred_map,
alpha=0.5,
label_info=label_color_dict,
return_ax=True,
)
plt.show()
使用特定于病理学的模型进行特征提取¶
在本节中,我们将展示如何使用 TIAToolbox 提供的 WSI 推理引擎,从 TIAToolbox 之外的预训练 PyTorch 模型中提取特征。为了说明这一点,我们将使用 HistoEncoder,一种特定于计算病理学的模型,它以自监督的方式训练以从组织学图像中提取特征。这个模型已在以下位置提供:
‘HistoEncoder: 基于数字病理学的基础模型’(https://github.com/jopo666/HistoEncoder),由赫尔辛基大学的 Joona Pohjonen 和团队开发。
我们将绘制一个特征地图的 umap 降维到三维(RGB)以可视化这些特征如何捕获上述某些组织类型之间的差异。
# Import some extra modules
import histoencoder.functional as F
import torch.nn as nn
from tiatoolbox.models.engine.semantic_segmentor import DeepFeatureExtractor, IOSegmentorConfig
from tiatoolbox.models.models_abc import ModelABC
import umap
TIAToolbox 定义了一个 ModelABC,它是一个继承了 PyTorch nn.Module 的类,并规定了一个模型应如何配置才能在 TIAToolbox 推理引擎中使用。histoencoder 模型并未遵循该结构,因此我们需要将其封装到一个类中,这个类的输出和方法符合 TIAToolbox 引擎的要求。
class HistoEncWrapper(ModelABC):
"""Wrapper for HistoEnc model that conforms to tiatoolbox ModelABC interface."""
def __init__(self: HistoEncWrapper, encoder) -> None:
super().__init__()
self.feat_extract = encoder
def forward(self: HistoEncWrapper, imgs: torch.Tensor) -> torch.Tensor:
"""Pass input data through the model.
Args:
imgs (torch.Tensor):
Model input.
"""
out = F.extract_features(self.feat_extract, imgs, num_blocks=2, avg_pool=True)
return out
@staticmethod
def infer_batch(
model: nn.Module,
batch_data: torch.Tensor,
*,
on_gpu: bool,
) -> list[np.ndarray]:
"""Run inference on an input batch.
Contains logic for forward operation as well as i/o aggregation.
Args:
model (nn.Module):
PyTorch defined model.
batch_data (torch.Tensor):
A batch of data generated by
`torch.utils.data.DataLoader`.
on_gpu (bool):
Whether to run inference on a GPU.
"""
img_patches_device = batch_data.to('cuda') if on_gpu else batch_data
model.eval()
# Do not compute the gradient (not training)
with torch.inference_mode():
output = model(img_patches_device)
return [output.cpu().numpy()]
现在我们有了封装器,我们将创建我们的特征提取模型,并实例化一个 DeepFeatureExtractor,以便我们可以在整个WSI上使用此模型。我们将使用前面相同的WSI,但这次我们将使用HistoEncoder模型从WSI的切片中提取特征,而不是为每个切片预测一些标签。
# create the model
encoder = F.create_encoder("prostate_medium")
model = HistoEncWrapper(encoder)
# set the pre-processing function
norm=transforms.Normalize(mean=[0.662, 0.446, 0.605],std=[0.169, 0.190, 0.155])
trans = [
transforms.ToTensor(),
norm,
]
model.preproc_func = transforms.Compose(trans)
wsi_ioconfig = IOSegmentorConfig(
input_resolutions=[{"units": "mpp", "resolution": 0.5}],
patch_input_shape=[224, 224],
output_resolutions=[{"units": "mpp", "resolution": 0.5}],
patch_output_shape=[224, 224],
stride_shape=[224, 224],
)
当我们创建 DeepFeatureExtractor 时,我们会传递 auto_generate_mask=True 参数。这将使用Otsu阈值法自动生成组织区域的掩码,从而提取器仅处理包含组织的切片。
# create the feature extractor and run it on the WSI
extractor = DeepFeatureExtractor(model=model, auto_generate_mask=True, batch_size=32, num_loader_workers=4, num_postproc_workers=4)
with suppress_console_output():
out = extractor.predict(imgs=[wsi_path], mode="wsi", ioconfig=wsi_ioconfig, save_dir=global_save_dir / "wsi_features",)
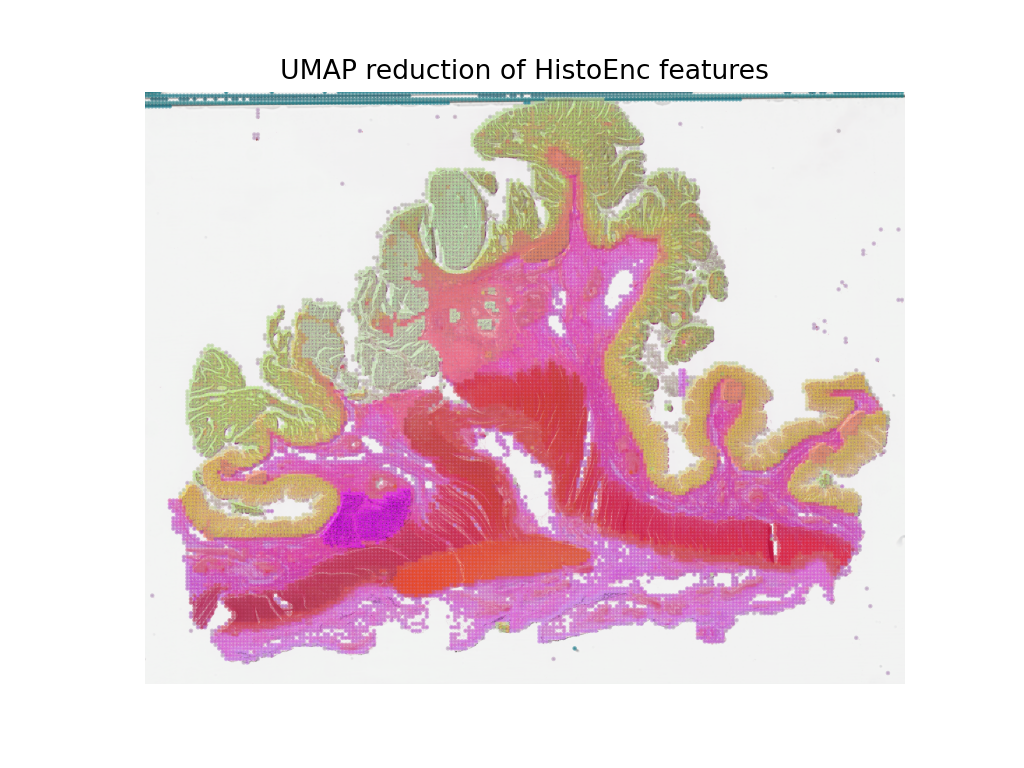
这些特征可以用于训练下游模型,但在这里,为了直观了解这些特征代表了什么,我们将使用UMAP降维在RGB空间中可视化这些特征。用相似颜色标记的点应具有相似的特征,因此当我们将UMAP降维叠加到WSI缩略图上时,可以检查这些特征是否自然分离到不同的组织区域中。在接下来的单元格中,我们将绘制它,以及之前的切片级预测图,以查看特征与切片级预测之间的比较。
# First we define a function to calculate the umap reduction
def umap_reducer(x, dims=3, nns=10):
"""UMAP reduction of the input data."""
reducer = umap.UMAP(n_neighbors=nns, n_components=dims, metric="manhattan", spread=0.5, random_state=2)
reduced = reducer.fit_transform(x)
reduced -= reduced.min(axis=0)
reduced /= reduced.max(axis=0)
return reduced
# load the features output by our feature extractor
pos = np.load(global_save_dir / "wsi_features" / "0.position.npy")
feats = np.load(global_save_dir / "wsi_features" / "0.features.0.npy")
pos = pos / 8 # as we extracted at 0.5mpp, and we are overlaying on a thumbnail at 4mpp
# reduce the features into 3 dimensional (rgb) space
reduced = umap_reducer(feats)
# plot the prediction map the classifier again
overlay = overlay_prediction_mask(
wsi_overview,
pred_map,
alpha=0.5,
label_info=label_color_dict,
return_ax=True,
)
# plot the feature map reduction
plt.figure()
plt.imshow(wsi_overview)
plt.scatter(pos[:,0], pos[:,1], c=reduced, s=1, alpha=0.5)
plt.axis("off")
plt.title("UMAP reduction of HistoEnc features")
plt.show()
我们看到,从切片级预测模型的预测图和我们的自监督特征编码器的特征图,都捕获了WSI中组织类型的相似信息。这是对我们模型按预期工作的一个很好的验证。这也表明由HistoEncoder模型提取的特征捕获了组织类型之间的差异,因此它们编码了与组织学相关的信息。
下一步做什么¶
在本笔记中,我们展示了如何使用``PatchPredictor``和``DeepFeatureExtractor``类及其``predict``方法来预测大块切片和WSI中切片的标签或提取特征。我们介绍了``merge_predictions``和``overlay_prediction_mask``辅助函数,这些函数将切片预测输出合并,并将生成的预测图作为叠加显示在输入图像/WSI上。
所有这些过程在TIAToolbox内进行,我们可以按照示例代码轻松拼接各个部分。请务必正确设置输入和选项。我们鼓励您进一步研究改变``predict``函数参数对预测输出的影响。我们已展示如何在TIAToolbox框架中使用您自己的预训练模型或研究社区提供的模型为特定任务在大型WSI上进行推理,即使模型结构未在TIAToolbox模型类中定义。
您可以通过以下资源了解更多信息: